免疫算法(Immune Algorithm)详解
关于免疫算法(IA),其功能与遗传算法、模拟退火等算法实现的功能是相同的,都是用来求最优解。例如求函数最值、旅行商问题等。从本质上说,免疫算法更像是遗传算法的一种延申。IA虽然其中借鉴了生物学(免疫学)的概念,但学习时需要注意,IA毕竟是一种算法,把算法中所有概念都与免疫学概念联系起来是容易难以理解算法的,甚至容易混淆。所以IA只是借鉴免疫学概念并受免疫过程的启发,最终其实还是需要回归到算法当中。
关于免疫算法(IA),其功能与遗传算法、模拟退火等算法实现的功能是相同的,都是用来求最优解。例如求函数最值、旅行商问题等。从本质上说,免疫算法更像是遗传算法的一种延申。IA虽然其中借鉴了生物学(免疫学)的概念,但学习时需要注意,IA毕竟是一种算法,把算法中所有概念都与免疫学概念联系起来是容易难以理解算法的,甚至容易混淆。所以IA只是借鉴免疫学概念并受免疫过程的启发,最终其实还是需要回归到算法当中。
即便如此,兔兔在后面还是需要将算法与一些生物学概念联系,但是会辨别其中本质区别。而且学习时需要与遗传算法相结合,毕竟免疫算法从某种角度来说是遗传算法的一种延申。
(1)相关免疫学知识与IA算法
根据高中的生物学知识,我们知道,抗原(细菌、病毒、疫苗等)进入生物体后,首先会被非特异性免疫消灭,但有时这种免疫防线会被突破。所以还有特异性免疫,即B细胞受抗原刺激后分化成浆细胞和记忆细胞,浆细胞分泌抗体抑制消灭抗原。记忆细胞在下次接受抗原时可以直接分化成浆细胞并分泌抗体,抑制抗原。
上面的概念虽然很多,但实际在算法中很多相关概念和过程是可以合并或忽略的。
在遗传算法中,我们把种群中的个体(即染色体)当作解,先初始种群(初始解),在进行交叉、突变、选择;这里的抗原、抗体在一开始时就代表初始解,抗原抗体在一开始是混在一起的,只不过我们把较优的一部分解叫“抗原”,不优的部分叫做”抗体“。之后的每次迭代过程我们叫做“打疫苗”。
在免疫学中,我们知道,当生物体接种疫苗后,相应的B细胞分化成浆细胞与记忆细胞,再次注射疫苗时记忆细胞在抗原刺激性又会分化成浆细胞,从而分泌更多的抗体。而且,免疫学中,抗原抗体,抗原与记忆细胞的识别是特异性结合的。在我们IA算法中,抗原抗体是几乎没有特异性结合这种过程的(有的文章中会把序列识别等当作特异性识别,其实是不准确的,不必在意)。而且,IA算法中几乎不区分浆细胞、记忆细胞、抗原这三者的概念的,或者说,这三者表示算法中同一个东西。算法中表示接种疫苗的过程是:把之前的抗原克隆复制(即把这些解复制多次),对这些克隆进行突变,选取较优的部分作新抗原(即新的较优解),再把这些抗原与新的疫苗抗体(即新的一些随机解)混合在一起(这个过程可以看作是接种疫苗),在从这些混合解中选取较优的部分作为新的抗原,这个新的抗原在进入下一次接种疫苗的过程中。在从混合解中选的过程中,我们也淘汰了一些不优的解,可以对应是抗体免疫抑制抗原(其中其实也包括了抗原复制扩增对抗体的一种抑制),但本质就是从中选较优的解,与是否是免疫抑制关系不是很大(但很多文章会是这样讲的)。
如果从现在来看的话,免疫算法与遗传算法区别并不是很大,主要就是除了之前的突变、交叉操作,多了一个接种疫苗的操作——即每次选一部分较优解(抗原、记忆细胞、浆细胞)复制选优后与随机解混合,从中选取较优解(抗原),再进行重复操作。
但是在免疫算法选择的步骤中,对遗传算法中由“适应度”进行选择的方法做了很大改进,引出了“亲和度”(affinity)、"抗体浓度"(density)、"激励度"(simulation)这三个在选择操作中的重要概念。其中的激励度是由亲和度与抗体浓度进行计算的。亲和度与抗体浓度是由这些解来计算的。
“亲和度”(affinty)本质上就是遗传算法中的“适应度”(fitness),所以亲和度本质上代表解与最优情况的接近程度。例如,当我们求函数f(x)的最大值时,亲和度就可以用f(x)来表示,f(x)越大,亲和度也就越大。
“抗体浓度”(density)本质上是一个解与集合中其它所有的解当中距离比较近(或者说比较相似)的解的个数,再除以集合中解的总数总数就是这个解的浓度,称作抗体浓度(准确来说就是浓度,因为集合是抗原抗体的混合)。那么怎么判断一个解与其它所有解距离较近的个数呢?
所以我们需要一种方法来度量距离,并且当距离小于某一个阈值(delta)时判断这个解就是其中一个离它比较近的解,否则不是。所以我们需要找到解直接的一种距离度量方法。(注;很多文章会说两个解之间的相似程度或距离叫做亲和度,并把计算距离或相似程度这个过程叫做亲和力计算,这样在算法中不太准确,而且会和前面那个亲和度概念弄混)。
距离度量方法
(1)实数编码的解。
对于实数编码的解,通常可以用欧氏距离来表示,如果是一维的数,就是两个数相减绝对值;如果是二维平面的点,就是平面两点距离公式:
多维的点以此类推。除了欧式距离,还有马式距离、闵式距离等,在多元统计、泛函分析等学科都有涉及,IA算法大多采用欧式距离。
(2)离散编码的解。
一般情况下,我们遇到的离散的解就是二进制的长串(兔兔在遗传算法中曾使用过,详解《遗传算法(GA)详解》一文)。如[0,1,1,1,0,0,1,0]。对于这种情况通常采用海明距离。
其中,ak,bk分布表示各自数组中位置k的元素(1或0)。这样两个链对应位置不一样的位置越多,距离就越远,很符合逻辑。
那么,现在我们找到了距离度量方法,当距离小于阈值delta时就认为两个解接近,然后累计该解与所有解距离近的个数,最后除以解的总个数就是该解的浓度了。
“激励度”(simulation)就是最终选择的评判标准了。激励度公式如下:
其中alpha通常是1,beta=2,实际可以根据需要进行调整。一个解的激励度越大,那么就越先优选。对应就是遗传算法在“适应度”——适应度越大,被选概率越大。只不过这里有了density一项的影响,只要simulation大,我们就一定选这个解,而不是以大的概率取选它。我们根据simulation选解的操作是:把解按照simulation的大小从大往小排,取其中simulation较大的前一半作为抗原(选较优解),后面一半全都不要;之后操作:克隆(把抗原复制多个),随机突变,再把这些计算simulation,按顺序排,取simulation较大的部分,与抗体疫苗混合(接种疫苗),把这个混合集合再计算simulation ,排序选较大的部分,就是新的抗体的,之后循环操作。
对simulation的理解
我们发现,如果让式子中beta一项为0,那么就是适应度(fitness),即每次选择适应度最大的解。而减去了beta*density,就说明density值越大,其simulation就越小,就越可能不被选中。而density代表了这个解与所有解中比较相近的解的个数。所以浓度越低,激励度会越好,越容易被选中。
变异操作
与遗传算法相同,免疫算法在每次对抗体克隆后会对所有克隆进行变异。对于二进制的数组,变异方法与遗传算法中变异操作一致。而对于实数编码,变异操作可以表示为:
rand是0~1随机数,如果小于pm(即以概率pm选择是否突变),就进行突变,表示定义域区间长度。大于pm就不突变。
关于交叉操作,在IA中也是可以有的,但是有了变异操作,又有接种疫苗的操作,导致每次都有很大的随机性,所以多数情况是可以不用交叉。交叉操作与遗传算法中交叉操作一致。
(2)算法总结
在网上或其它文章中我们都可以看到关于免疫算法的流程图,而且有很多种,里面大多都是免疫学的概念,但其实回到算法当中,无外乎都是同种东西。所以关键还是算法流程,免疫学概念可以用来进行比喻帮助记忆。
(1)先初始n个解,n为种群个数。
(2)计算这些种群的亲和度、浓度,并计算出激励度。
(3)根据激励度对种群由大到小排列,取前n/2个做抗原,后面的不要。
(4)对抗原进行克隆,克隆m份,对mn/2个克隆进行变异。
(5)变异后计算亲和度、浓度,并计算激励度。根据激励度大小从大到小排列,取前n/2个做抗体。
(6)随机产生n/2个种群(即疫苗、抗体),与前面得到的抗体混合。
(7)混合后计算亲和度、浓度,并计算激励度,根据激励度从大到小排列,取前n/2做抗体。
(8)得到的抗体再回到(4),重复循环。
(9)在循环结束后,根据affinity排序,选取affinity最大的那个解作为最优解。
以上就是免疫算法的基本流程。
(3)算法实现
我们以求函数f(x)=sin(3x) ()求最大值为例。我们编码解的二进制数组长度binarylength为8,初始种群数popsize=40,突变概率pm为0.7,阈值delta=3,克隆数clone_num为10,alpha=1,beta=1,循环次数circle=30。
import numpy as np
class IA:
def __init__(self,circle=30,pm=0.7,alpha=1,beta=1,delta=3,popsize=40,binarylength=8,area=4,clone_num=10):
self.circle=circle #循环次数
self.pm=pm #突变概率
self.clone_num=clone_num #克隆数
self.alpha=alpha
self.beta=beta
self.delta=delta #阈值
self.binarylength=binarylength #二进制数组长度
self.pop=np.random.randint(0,2,size=(popsize,binarylength)) #随机初始popsize个种群
self.area=area #即domain of definition,定义域,这里简写成area
def bin_to_dec(self,pop):
'''把种群中所有二进制数组转换成0~4之间的十进制数'''
n=pop.shape[0]
p=pop.shape[1]
s=np.zeros(shape=(n,1))
for i in range(self.binarylength):
s+=pop[:,i].reshape(n,1)*2**(p-i-1)
return self.area*s/2**p
def mutation(self,pop):
'''进行变异操作'''
n,p=pop.shape
for i in range(n):
if np.random.rand()<self.pm:
point=np.random.randint(0,p) #随机选位点突变
if pop[i,point]==1:
pop[i,point]=0
else:
pop[i,point]=1
return pop
def simulation(self,affinity,density):
计算激励度
return self.alpha*affinity-self.beta*density
def density(self,pop):
'''计算浓度'''
n,p=pop.shape
den = [] #用来储存每一个解对应浓度
j=0
for i in range(n):
judge=0 #保存所有与i点距离达到阈值的个数
for j in range(n):
s=0 #保存二进制数组中对应位置数字不同的个数
for k in range(p):
if pop[i,k]==pop[j,k]:
s+=1
if s<self.delta: #判断是否达到阈值
judge+=1
den.append(judge)
return np.array(den)/n
def affinity(self,pop):
'''亲和度计算'''
p=self.bin_to_dec(pop=pop)
p=p.reshape(1,-1)[0]
p=p.astype('float') #转换数据类型,否则np.sin(3*p)会报错
return np.sin(3*p)
def main(self):
'''主程序'''
initpop=self.pop #初始化种群
density=self.density(pop=initpop)
affinity=self.affinity(pop=initpop)
simulation=self.simulation(affinity,density)
index=np.argsort(-simulation) #根据激励度从大到小排序
pop=initpop[index]
n,p=pop.shape
best_pop = pop[0:int(n / 2), :] #选出前n/2作为抗体
#开始进行circle次循环操作
for c in range(self.circle):
print('the {} circle'.format(c)) #显示循环次数
clone=best_pop
for i in range(self.clone_num-1): #开始进行克隆
clone=np.r_[clone,best_pop]
clone=self.mutation(pop=clone) #对克隆变异
clone_density=self.density(pop=clone)
clone_affinty=self.affinity(pop=clone)
clone_simulation=self.simulation(affinity=clone_affinty,density=clone_density) #计算激励度
index=np.argsort(-clone_simulation) #根据激励度排序
newpop=clone[index][0:int(n/2),:] #选出抗体
antigen=np.random.randint(0,2,size=(int(n/2),p)) #随机初始一些解做抗原
combin_pop=np.r_[newpop,antigen] #把抗原抗体结合
density=self.density(pop=combin_pop) #计算结合后的浓度
affinity=self.affinity(pop=combin_pop)
simulation=self.simulation(affinity,density)
index=np.argsort(-simulation)
combin_pop=combin_pop[index][0:int(n/2),:]
best_pop=combin_pop #选出抗体,回到初始步骤进行循环
return best_pop
if __name__=='__main__':
ia=IA()
best_pop=ia.main()
result=ia.bin_to_dec(pop=best_pop) #把结果转换成十进制数
x=np.arange(0,4,0.1)
y=np.sin(3*x)
plt.plot(x,y) #画函数图像
plt.scatter(result,np.sin(3*result),color='red') #画解的散点图
plt.show()程序运行结果如下:
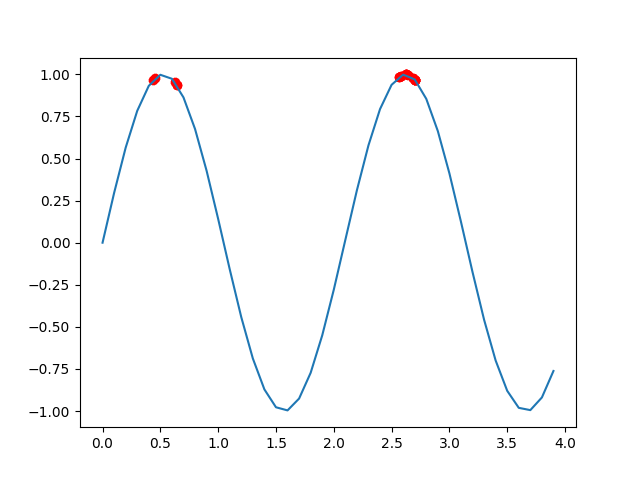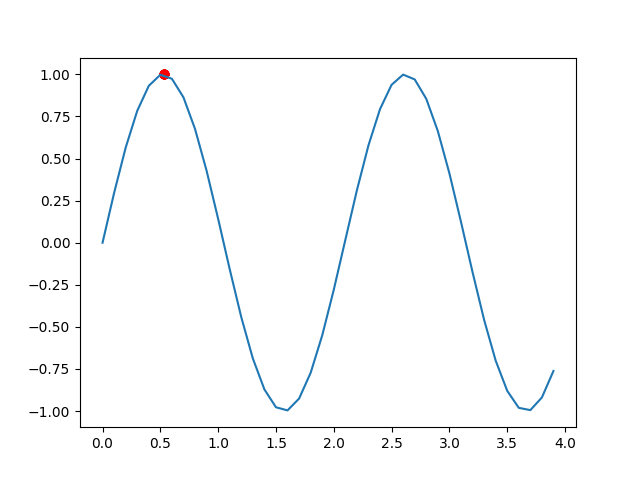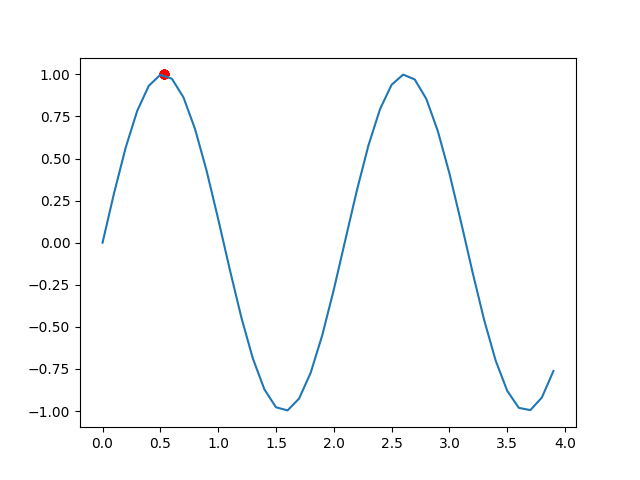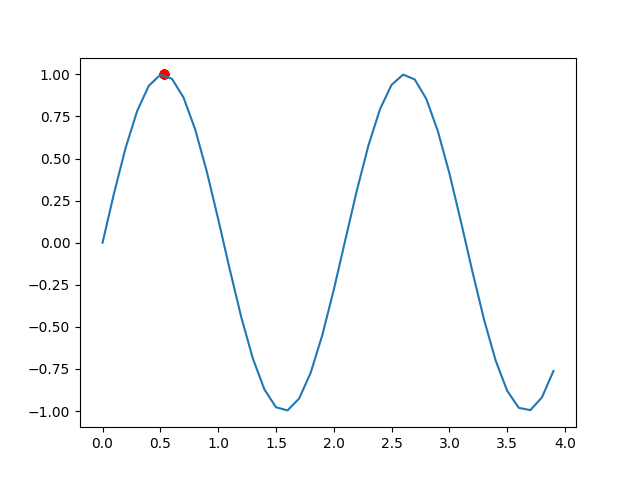
我们可以看到,结果很快就在最大值附近了,说明效果很好。
值得注意的是,随着循环的进行,结果离最优越来越近,我们这时应该逐渐减小变异概率pm,当达到最优时,我们是不希望他变异很大,这样不容易稳定在最优解,所有可以设置pm[i]=pm0/c[i],即第i次循环的变异概率为初始的突变概率pm除以循环次数。
对于求二元函数最值,我们一般按照实数编码的方式,很少用二进制编码。过程也是相同的,只是相似的(距离)度量一般采用欧式距离,阈值通常也比较小。
(4)总结
免疫算法从本质上说是遗传算法的一种延申,而遗传算法更像是对蒙特卡罗模拟的一种改进。在蒙特拉罗模拟中,我们只是随机初始解并选择最优;在遗传算法中,由于交叉于变异的出现,使得解有很大的随机性并可以找到最优,并在选择中以大的概率保留下来;在免疫算法中,由于接种疫苗过程的出现,以及基于亲和度、浓度计算出的激励度的选择方法,使得随机性比遗传算法更大,同时也能够很好地达到全局最优。
更多推荐
 已为社区贡献21条内容
已为社区贡献21条内容









所有评论(0)